PLASMID-
advertisement

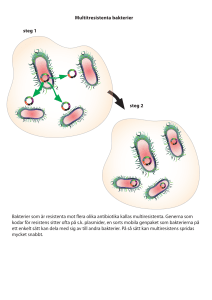
PLASMIDPREPARATION (”Plasmidlab”) Laborationshandledning Läkarprogrammet T1 Apotekarprogrammet T2 Biovetenskapliga läkemedelsprogrammet T2 Tandläkarprogrammet T2 Rev. 2004-02-17 INTRODUKTION Dagens genteknologi fick sitt genombrott på 1970-talet och har kommit att revolutionera den biomedicinska forskningen. Genom att utnyttja bakteriella system har man lärt sig att ”klona” gener; man kan numera isolera masskopierade främmande DNA-sekvenser ur bakteriekulturer. Kloningsteknologin har redan inneburit stora praktiska medicinska framsteg. Ett av de främsta exemplen är humant insulin producerat av bakterier. Två slags bakteriella ”verktyg” är avgörande vid genkloning: plasmider och restriktionsenzymer. Plasmider Plasmider förekommer naturligt och kan ses som extra ”minikromosomer” i bakterier. Ofta innehåller ”vilda” plasmider gener för antibiotikaresistens, vilket utnyttjas i de plasmidvektorer, modifierade plasmider, som används som DNA-bärare vid kloning. Främmande DNA sätts då in i plasmidvektorn som sedan förs in i (”transformation”) och odlas i bakterier. Antibiotikaresistensen fungerar som selektionsmarkör: Genom att den gen som ska klonas sätts in i en vektor som också uttrycker t ex ampicillinresistens kan man vara säker på att endast de bakterier som tagit upp plasmidvektorer överlever då de odlas med ampicillin (”negativ selektion”, icke transformerade celler väljs bort). Plasmidvektorn pTZ19R innehåller betalaktamasgenen, ”bla”, som ger resistens mot ampicillin. Vektorn är en ”phagemid” som kan förökas i bakterier som plasmid eller bakteriofag (virus) med replikationsstart från ”rep(pMB1)”- respektive ”f1(IG)”-sekvenserna. Främmande DNA kan ligeras i polylinkern ”MCS” (Multiple Cloning Site) som infogats i lacZ-genen, vilket möjliggör ”blue/white screening” (se text). Plasmidkartan visar också unika restriktionssites utanför polylinkern. 2 En av de första kommersiella plasmidvektorerna var pBR322 som innehåller gener för resistens mot ampicillin och tetracyklin. I denna laboration ska vi arbeta med vektorn pTZ19R som utvecklats ur pBR322 men endast bär ampicillinresistensgenen. I likhet med de flesta plasmidvektorer har pTZ19R en ”polylinker” där främmande DNA som ska klonas kan ligeras in. Polylinkern består av en uppsättning unika restriktionssites, igenkänningssekvenser för olika restriktionsenzymer. ”Unik” avser här att sekvensen bara finns på ett ställe i plasmiden. Polylinkersekvensen i pTZ19R. I en av de plasmider som används vid laborationen har DNA klonats i BamHI-sitet. Restriktionsenzymer Vilda bakterier uttrycker restriktionsenzymer, vilkas funktion är att bryta ner främmande DNA, t ex virus, som tagit sig in i cellen. Restriktionsenzymerna är proteiner som känner igen och klyver båda DNA-strängarna vid specifika sekvenser. Bakteriens eget DNA kan skyddas antingen genom att restriktionsenzymernas igenkänningssekvenser maskeras kemiskt, genom metylering, eller genom att igenkänningssekvenser helt enkelt saknas i bakteriens arvsmassa. Laboratoriestammar av kolibakterier (Escherichia coli) som används vid genkloning saknar egna restriktionsenzymer så att de inte kan bryta ner det främmande DNA man vill klona. Vid genkloning öppnas en plasmidvektor i polylinkern med hjälp av restriktionsenzym som väljs så att vektorns ändar blir förenliga med ändarna på det DNAfragment man vill klona. Vissa enzymer klyver så att DNA-ändarna blir jämna (”blunt ends”) medan andra lämnar ett överhäng av enkelsträngat DNA (”sticky ends”). Om man använder två restriktionsenzymer som ger olika DNA-ändar efter klyvning kan man också bestämma åt vilket håll DNA-fragmentet ska sitta i vektorn (”forced cloning”). Vektor och fragment fogas samman kovalent med hjälp av ett annat enzym, DNA ligas, varefter det ligerade DNA:t kan användas för transformation av bakterier. Det är enklare att ligera ”sticky ends” eftersom de fäster ihop genom basparning (vätebindningar) redan innan man tillsätter DNA-ligas. SELEKTION VID PLASMIDKLONING Då främmande DNA ligeras med plasmidvektorer bildas inte bara den önskade produkten utan också oönskade biprodukter, t ex återförslutna tomma vektorer och linjära multimerer. Vid transformationen tas alla slags ligeringsprodukter upp av bakterier men bara cirkulariserade plasmider kan replikeras och uttrycka sin 3 antibiotikaresistens. Bakterier som bara tagit upp lösa DNA-fragment kommer därför inte att överleva då man tillsätter antibiotika i odlingsmediet (”negativ selektion”). -GATAAGAGCTCGGTACCCGGGATCCTGACT-CTATTCTCGAGCCATGGGCCCTAGGACTGA- polylinker SacI pTZ19R BamHI restriktionsklyvning -GATAAGAGCT -CTATTC GATCCTGACTGACTGACGGTACCCGG TCGAGCCATGGGCCCTAG -GATAAGAGCT -CTATTC GATCCTGACTGACTGACGG-gensekvens->-CGG TCGAGCC--------------GCCCTAG DNA fragment med kompatibla ändar T4 DNA ligas ligering SacI -GATAAGAGCTCGG-gensekvens->-CGGGATCCTGACT-CTATTCTCGAGCC--------------GCCCTAGGACTGAInligerad gen pTZ19R BamHI Exempel på ”forced cloning”. Genom att använda två olika restriktionsenzymer kan man bestämma åt vilket håll ett DNAfragment med förenliga ändar kommer att ligeras med vektorn. Blue/white-screening Tack vare antibiotikaresistensen överlever bakterier som tagit upp cirkulära plasmidvektorer vid odling med antibiotika. Det gäller oavsett om plasmiderna är rekombinanta (plasmid + främmande DNA) eller tomma (polylinkern återligerad utan ”insert”). För att hitta de bakteriekolonier som innehåller rekombinanta vektorer använder man sig ofta av ”blue/white screening” som positiv selektion. Man utnyttjar då bakterier med ett defekt β-galaktosidas, det enzym som normalt bryter ned laktos (mjölksocker). Vektorn bär genen lacZ’ som kodar för α-domänen av β-galaktosidas. Uttrycket av lacZ’ kontrolleras av sekvenser från lac-operonet som sitter uppströms i 4 vektorn. I närvaro av laktos aktiveras genen och den uttryckta proteindomänen ger värdbakterien ett funktionellt β-galaktosidas. Detta kallas α-komplementering. I praktiken används inte laktos utan laktosanalogen IPTG (isopropyltiogalaktosid) som inte kan brytas ned av β -galaktosidas och därför ger en bestående aktivering av lacZ’. För att man dessutom ska kunna se galaktosidasaktiviteten i bakterierna tillsätts ytterligare en laktosanalog, X-gal (5-brom-4-klor-3-indolyl-α-D-galaktopyranosid) som bryts ned av β -galaktosidas till ett blått färgämne (5-brom-4-klor-3-indol). Bakterier som uttrycker aktivt β-galaktosidas kommer därför, i närvaro av X-gal, att färgas blå. Metoden gör det möjligt att se vilka bakteriekolonier som innehåller rekombinanta vektorer eftersom polylinkern, där främmande DNA ligeras i vektorn, sitter i början av lacZ’-genens kodande sekvens. I rekombinanta vektorer skiljs lacZ’-sekvensen från sin promoter av det införda främmande DNA:t och kan därför inte längre uttryckas. Därmed förhindras α –komplementering; bakterier med rekombinanta plasmider kan inte bryta ner X-gal utan förblir vita. Från tomma vektorer uttrycks lacZ’ obehindrat, X-gal kan brytas ner och bakteriekolonier färgas blå. GELELEKTROFORES Vid gelelektrofores separeras molkyler av olika storlek genom att de olika lätt tar sig igenom en porös gel i ett elektriskt fält. För elektrofores av DNA brukar man tillverka en gel av polysackariden agaros som ”smälts” genom uppvärmning i en buffertlösning och sedan stelnar till en gel då den svalnar. För elektroforesen placeras sedan gelen i ett bad av samma buffert, som ju leder ström eftersom den är en jonlösning. Bufferten ska vara lätt basisk så att fosfatryggraden i DNA deprotoneras. Allt DNA som sätts på gelen kommer då att hållas negativt laddat och vandra genom gelen mot den positiva polen. För att man ska kunna se hur DNA:t separerats tillsätts också etidiumbromid i buffertlösningen. Etidiumbromid kilar in sig mellan baserna i DNA och eftersom ämnet fluorescerar i UV-ljus kommer man att kunna visa var på gelen det finns DNA. Då man elektroforerar plasmid-DNA är det inte bara storleken i baspar räknat som avgör hur DNA vandrar i gelen. Bakterier packar sitt DNA, även plasmider, genom supercoiling, vilket ger en kompakt ”ihopsnodd” struktur. Vid plasmidpreparationen kommer vanligen en mindre del av plasmiderna att få slumpmässiga mekaniska enkeloch dubbelsträngsbrott. Vid enkelsträngsbrott ”lossnar” supercoilingen då DNAsträngarna vid brottpunkten kan röra sig runt varandra. Man får en ”relaxad” cirkulär plasmid. Vid dubbelsträngsbrott lineariseras plasmiden, men till skillnad från en restriktionsklyvning kan brottet sitta var som helst i sekvensen. Relaxat och linjärt DNA upptar en större volym än supercoilat och kommer därför att röra sig långsammare vid elektrofores. 5 Elektronmikrografier av mitokondriellt DNA. Överst en relaxad cirkulär form. Frånvaron av supercoiling kan ha orsakats av enkelsträngsbrott. Därunder en mer kompakt, supercoilad form. Bakterier packar sitt DNA, såväl kromosom som plasmider, på samma sätt. 6 LABORATIONENS UPPLÄGGNING Ni kommer att få en blandning av två olika plasmider, dels den tomma vektorn pTZ19R och dels samma vektor med ett klonat 1500 bp DNA-fragment i polylinkerns BamHI-site. (Blandningen kan tänkas motsvara resultatet av en ligeringsreaktion.) Plasmidmixen används för att transformera kolibakterier, som sedan får växa på agarplattor innehållande ampicillin, IPTG och X-gal. Varje grupp ska plocka två blå och två vita bakteriekolonier för att preparera plasmiderna ur dessa. Prover av plasmiderna ska sedan klyvas med BamHI och analyseras med agarosgelelektrofores för att kontrollera vektorns och det klonade fragmentets storlekar. UTFÖRANDE Dag 1: Transformering av E.coli med plasmid-DNA. 1. Sätt 100µl tinad cellsuspension till röret med 10µl plasmidblandning. Blanda försiktigt med hjälp av pipett. 2. Inkubera på is i 25-30 minuter. 3. Värmebehandla cellerna (”heat shock”) på värmeblock, 37°C, i exakt tre minuter. 4. Kyl cellerna på is i någon minut. 5. Tillsätt 1 ml LB-medium. 6. Märk en LB-agarplatta och sprid ut cellblandningen på den. (Luta plattan åt olika håll så cellerna sprids så bra som möjligt.) 7. Plattan inkuberas i värmeskåp, 37°C, över natt. Dag 2: Plockning av bakteriekolonier och odling av bakterier. 1. Hämta agarplattan från dag 1 samt fyra 50 ml Falconrör med 5ml LB-medium (ampicillin, 100 µg/ml). 2. Plocka två vita och två blå kolonier från agarplattan. Använd tandpetare som hålls med en steriliserad pincett. (Det räcker att nudda kolonin med tandpetaren.) Släpp ner tandpetarna i varsitt Falconrör och skruva åt locken ordentligt. Märk rören. 3. Rören inkuberas i skak, 37°C, över natt. 7 Dag 3: Plasmidpreparation, restriktionsklyvning och agarosgelelektrofores. PLASMIDPREPARATION 1. Skörda buljongkulturerna genom att pipettera över 1,5 ml från varje Falconrör till varsitt mikrofugrör (”Eppendorfrör”). Centrifugera fem minuter i bordscentrifug. OBS! Balans i centrifugen! 2. Tag av supernatanterna och fyll upp mikrofugrören med mer bakteriebuljong för att få en större bakteriepellet. Centrifugera igen. 3. Tag av supernatanterna. Fyll på mer bakterier om det behövs. (Fråga assistent!) 4. Resuspendera bakteriepelletarna i 250 µl buffert G1. Suspensionen ska vara homogen (inga klumpar kvar). 5. Lysera cellerna genom att tillsätta 250 µl av lösning G2. Blanda noga, men försiktigt, genom att vända mikrofugrören flera gånger. Låt rören stå fem minuter. 6. Neutralisera proverna genom att tillsätta 350µl av lösning G3. Blanda åter noga men försiktigt. (Proverna ska nu ”skära sig”.) Centrifugera tio minuter. 7. Pipettera över supernatanterna till spinnkolonnerna. Centrifugera en minut för att ladda proverna på kolonnerna. Häll bort ”flowthrough:n”. 8. Tvätta kolonnerna med 500 µl av lösning G4. Centrifugera en minut. 9. Häll bort tvättlösningen och centrifugera kolonnerna igen för att få dem helt torra. 10. Flytta över kolonnerna till nya mikrofugrör. Tillsätt 75 µl dH2O (destillerat vatten) i varje kolonn. Pipettera direkt mot kolonnens kiselmatrix men undvik att komma åt det med pipettspetsen. Eluera kolonnerna genom att centrifugera i två minuter. Solution G1 (Cell Suspension) Store at 4°C 50 mM Tris/Cl (pH 8.0); 10 mM EDTA; 100 µg/ml RNase A Solution G2 (Cell Lysis) Store at RT 200 mM NaOH; 1% SDS (w/v) Solution G3 (Neutralization/Binding) Store at RT Contains acetate and guanidine hydrochloride Solution G4 (Wash, reconstituted) Contains ethanol, NaCl, EDTA, and Tris/HCl Store at RT Vi använder ”JETquick Plasmid Miniprep Spin Kit” från GENOMED. Detta är lösningarnas sammansättning som tillverkaren deklarerat dem. 8 RESTRIKTIONSKLYVNING 1. Gör en arbetslösning av restriktionsenzymet BamHI. Blanda först 10 µl ”10X BamHI-buffert” med 38 µl ddH2O i ett mikrofugrör och tillsätt sedan 2 µl BamHI-enzym (totalt 50 µl). Enzymet måste förvaras kallt hela tiden. Blanda arbetslösningen noga och centrifugera ner ev droppar. 2. För över 10 µl av varje plasmidpreparation till nya märkta mikrofugrör och tillsätt 10µl av BamHI-arbetslösningen till varje rör. 3. Inkubera rören vid 37°C i minst 45 minuter. 4. Blanda oklyvda kontrollprover genom att blanda 10 µl av varje plasmidpreparation med 2 µl ”6X gel-loading buffer” i märkta mikrofugrör. 5. Sätt 4µl ”6X gel-loading buffer” till de klyvda proverna. AGAROSGELELEKTROFORES 1. 2. 3. 4. Väg upp 1 g agaros i en 200 ml E-kolv. Tillsätt 100 ml TAE-buffertlösning. Smält agarosen i mikrovågsugn. (Kör tills det kokar.) Låt agarossmältan svalna tills man nästan inte bränner sig på kolven längre . Tillsätt en droppe etidiumbromidlösning. OBS! Etidiumbromid är mutagent. Använd handskar. Gäller även vid hantering av gelen! 5. Häll agarosen i gelinsatsen och placera ut kammar för brunnarna. 6. Låt gelen stelna (ca 30 minuter). 7. Ta bort kammarna (försiktigt så inte brunnarna skadas). 8. Vänd gelinsatsen i elektroforesapparaten och häll i TAE-buffert så att det täcker gelen. 9. Ladda klyvda prover och oklyvda kontrollprover, 10 µl av varje prov. Håll pipettspetsen rakt ovanför brunnen och låt provet sjunka genom TAEbufferten. Ladda även storleksmarkör i en brunn. Notera i vilken ordning proverna laddas. 10. Sätt spänningen på 120V och låt elektroforesen gå i 60 minuter. 11. Fotografera gelen under UV-ljus. (Etidiumbromiden interkalerar, ”kilar in sig”, mellan kvävebaserna i DNA och ger upphov till fluorescens vid UVbelysning.) 9