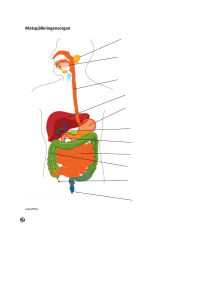
Naturliga populationer i Trollsvattnen
advertisement

Syfte? Inblick i vanlig genotypbestämningsmetod Allozymer har ofta använts som genetisk markör vid populationsgenetiska studier Eko-genetisk långtidsstudie Studera genetisk variation inom och mellan populationer – används inom bevarandebiologin Naturliga och introducerade populationer av öring Länsstyrelser får ofta ta del av den här typen av genetiska data. Man bör veta hur dessa är framtagna och själv ha sett hur data ska tolkas Tre vattensystem Vävnadsprover för genetisk analys Naturliga populationer i Trollsvattnen Två sympatriskt existerande kryptiska populationer Otoliter för åldersbestämning • Undersöka morfologiska skillnader • Populationernas utbredning i vattensystemet • Statistiska styrka att upptäcka kryptisk populationsstruktur • lika frekvens • stabil sympatri i 20 år • inga uppenbara fenotypiska skillnader 1 Bävervattsprojektet Utplantering 1979 1000 indivder per stam Diagnostiskt locus AGP-2 Identifiering av hybrider Lillrörtjärnen (66) Rena stammar och F1 hybrider identifieras i locus AGP-2 E4 (83) Tjärn 2 Östra (57) Stora Bävervattnet 1025) E3 (54) Lilla Bävervattnet (760) E2 (45) E1 (55) Djuptjärnen (57) Stam A Storvuxen Kallsjön Stam B Småvuxen Fälpfjälltjärnarna Haravattnet (588) Senare generationer svårare att identifiera. Haraån (42) Lillrörtjärnen (66) NEWHYBRIDS Klassificerar individer till sex grupper. E4 (83) Tjärn 2 Östra (57) Stora Bävervattnet 1025) F1 E3 (54) Lilla Bävervattnet (760) E2 (45) E1 (55) Djuptjärnen (57) Stam A Stam B F2h F1hxA F1h F2 Haravattnet (588) Haraån (42) Sammanfattade resultat • Stam A och B har etablerat sig på olika lokaler i sjösystemet i olika utsträckning. • Hybrider går inte att identifiera och klassificera i flera generationer med nuvarande markörer och testade program NewHybrids Structure GeneClass • Stammarna kan ha hållits reprodultivt åtskilda i viss utsträckning. Proteinelektrofores (allozymer) Olika “varianter” av samma enzym (protein) - uttrycks på basis av gener i cellkärnans DNA Olika alleler ger upphov till olika allozymer, vilka vanligtvis har olika elektrisk laddning och därför kan särskiljas genom elektrofores Bandmönster i en gel (med spänning) kan tolkas genetiskt: antal alleler i detta locus (oftast två) • homozygot – heterozygot • Vi studerar alltså inte DNA direkt... 2 Vad händer på lab? 4. Körning av gelelekrtofores 1. Förberedelse av vävnadsprov 2. Gjutning av geler 5. Slicing (uppskärning) av gelen 3. Applicering av enzymextrakt på gel 6. Infärgning och avläsning ENZYMELEKTROFORES – ”kom i håg-lista” Gen = specifik del av en DNA-molekyl Locus = fysiska positionen av genen på DNA-strängen, tex AGP-locus Allel = varianter av en gen Protein Enzym = protein som katalyserar reaktioner, tex AGP Aminosyrakedjor = ”bygger upp” enzym Allozym = en viss slags enzym, representerar olika alleler av samma gen Är det någon genetisk skillnad mellan öringar från de tre olika lokalerna? MONOMERT ENZYM – består av 1 aminosyrasekvens (t.ex. PEPLT) DIMERT ENZYM – består av 2 aminosyrasekvenser (t.ex. AGP) - Den ena homozygoten har bara den ena varianten av enzymet i cellkärnan - Den andra homozygoten har bara den andra varianten av enzymet i cellkärnan - Heterozygoten har båda varianterna av enzym i cellkärnan får därför två band Två genprodukter måste sättas ihop för att bilda ett fungerande enzym. Om enzymet består av två likadana genprodukter homodimer Om enzymet består av två olika genprodukter heterodimer Ex. med 2 alleler - Den ena homozygoten bildar bara ”dubletter” av den ena varianten - Den andra homozygoten bildar bara ”dubletter” av den andra varianten - Heterozygoten har båda varianterna i cellkärnan och bildar därför alla slags ”dubletter” Hos en heterozygot finns homo- respektive heterodimererna i mängdförhållandet 1:2:1 A1A1 A1A2 A2A2 Ex. med 2 alleler (kan också finnas med fler alleler) Ex. med 3 alleler A1A1 A1A2 A2A2 A1A3 A2A3 A3A3 A1A1 A1A2 A2A2 3 kodande TETRAMERT ENZYM – består av 4 aminosyrasekvenser (LDH-1) icke-kodande Hos en heterozygot finns de olika enzymvarianterna i mängdförhållandet 1:4:6:4:1 Exoner Ex. med 2 alleler (kan också finnas med fler alleler) A1A1 A1A2 Introner Regulatoriska regioner rDNA histoner A2A2 Kärn-DNA Mini- och mikrosatellit DNA icke-repetetivt (ex. ...GCATACTAGGA...) repetetivt (ex. ATT ATT ATT ATT ATT...) Annat repetitivt DNA mtDNA AGG - mikrosatellit Separation och visualisering (sekvensator) F-statistik kom-ihåg lista Mikrosatelliter - tolkning Observerad heterozygositet Förväntad heterozygositet enligt Hardy Weinberg FST Genetisk differentiering mellan populationer, 0=ingen differentiering, 1=fixering för olika alleler. FIT Avvikelser från Hardy-Weinberg i totalpopulationen FIS Avvikelser från Hardy-Weinberg i subpopulationerna Ho He Infärgning av primers - visualisering LOCUS 1 Ind 1 Heterozygot 93/99 Ind 2 Homozygot 103/103 Ind 3 Heterozygot 99/103 4 Lokal Genepop on the Web Locus Individ Polymorfigrad Heterozygositet Skillnader mellan lokaler (FST) Hardy-Weinberg Populationsgenetiska analyser Ladda upp filer med genotypdata Allozymer Microsatelliter Resultat: Scrolla ner! Klicka i önskade alternativ Svar som HTML Ladda upp fil med genotyper Den intressanta informationen finns oftast längst ner i filen 5